Bei der Proteinreinigung werden Nukleinsäuresequenzen, die für Proteine kodieren, durch gentechnische Verfahren in Wirtszellen eingebracht, wodurch sie in großen Mengen exprimiert werden. Anschließend werden sie in vitro mithilfe geeigneter Reinigungsmethoden gereinigt, um Proteine mit hoher Reinheit, Aktivität und Ausbeute zu erhalten . Proteinexpressionssysteme können in prokaryotische Systeme und eukaryotische Systeme eingeteilt werden.
Nachfolgend werden die Prinzipien und Methoden zur Induktion der Proteinexpression in prokaryotischen Systemen und zur In-vitro-Reinigung von Proteinen mithilfe der Affinitätschromatographie beschrieben.
PRINZIP
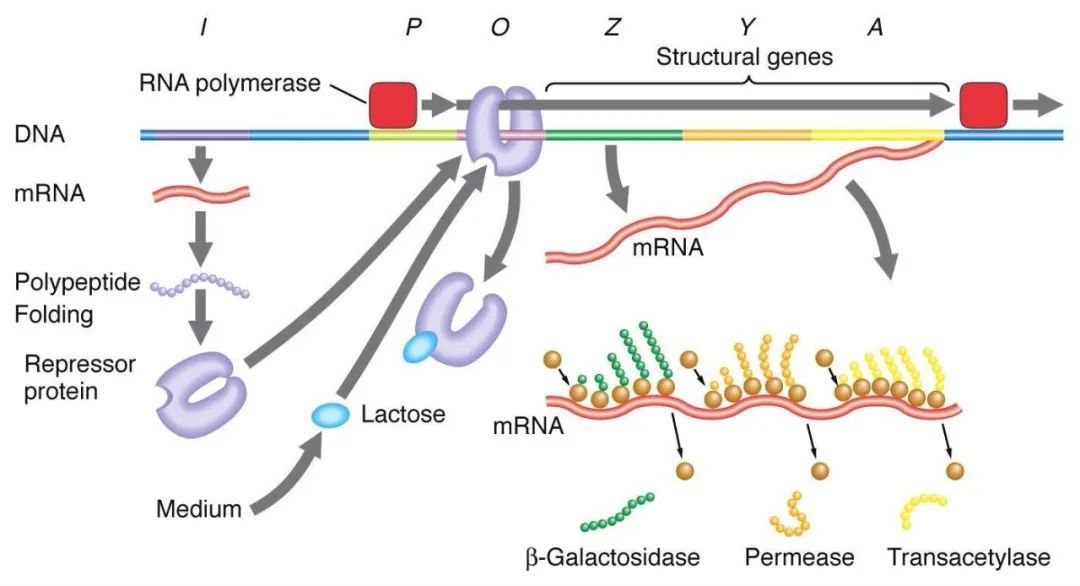
1、Negative Regulierung des Laktosemanipulators:
In Abwesenheit von Laktose befindet sich der Lac-Manipulator in einem Abschreckungszustand. Zu diesem Zeitpunkt exprimiert die I-Sequenz das Lac-Abschreckungsprotein, um an die O-Sequenz zu binden, wodurch die Bindung der RNA-Polymerase an die P-Sequenz verhindert und die Transkriptionsinitiierung gehemmt wird. Wenn Laktose vorhanden ist, gelangt Laktose in die Zelle und wird durch β-Galaktosidase katalysiert und in Isolaktose umgewandelt, die an das Hemmprotein bindet, was zu einer Konformationsänderung im Protein führt und zur Dissoziation des Hemmproteins von der O-Sequenz führt, wodurch die Transkription eingeleitet wird.
Isopropylthiogalactosid (IPTG) wirkt auf die gleiche Weise wie Isogalactose und ist ein äußerst wirksamer Induktor, der von Bakterien nicht verstoffwechselt wird, sehr stabil ist und daher in Laboratorien häufig verwendet wird.
2、Auswahl des Wirtsstamms:
(1) BL21 ist einer der am häufigsten verwendeten Stämme für die prokaryotische Expression. Er eignet sich hauptsächlich für die Expression ungiftiger Proteine mit E. coli-Polymerase und kann daher für die Expression prokaryotischer Systeme mithilfe von E. coli-RNA-Polymerase wie tac oder trc (z. B. pGEX-, pMAL-Plasmide) verwendet werden.
(2) BL21(DE3) integriert das T7-Phagen-RNA-Polymerase-Gen in der λ-Phagen-DE3-Region auf dem Chromosom des BL21-Stamms, der sowohl T7-RNA-Polymerase als auch E. coli-RNA-Polymerase exprimieren kann und für die Expression von Plasmiden wie der pET-Serie, pGEX, pMAL usw. verwendet werden kann.
3, Proteinreinigungsmethoden:
(1) Gelfiltrationschromatographie: Entsprechend der Molekülgröße aus der Mischung, um Proteine zu trennen, der Form verschiedener Proteine und der Molekülgröße der Unterschiede in der Mischung durch die Gelfiltrationschromatographiesäule, die Füllpartikel enthält, aufgrund der Molekülgröße verschiedener Proteine sind unterschiedlich, die Diffusion in die spezifische Größe der Aperturpartikel der Fähigkeit variiert, je größer die Proteinmoleküle sind, die zuerst eluiert werden, desto kleiner sind die Moleküle, je später, desto später die Elution.
(2) Ionenaustauschchromatographie: Die Proteintrennung und -reinigung basiert auf den unterschiedlichen Ladungen auf der Oberfläche des Proteins. Die Oberfläche des Proteins ist normalerweise gleichmäßig geladen und kann unter bestimmten Bedingungen mit Kationen-/Anionenaustauschsäulen kombiniert werden. Bei Änderung des pH-Wertes oder Verwendung eines Puffers mit allmählich zunehmender Ionenstärke zur Elution kann die gebundene Substanz mit den Ionen im Eluenten ausgetauscht und in die Lösung eluiert werden. Da verschiedene Substanzen unterschiedliche Ladungen und unterschiedliche Bindungsfähigkeiten mit der Ionenaustauschersäule aufweisen, ist auch die Reihenfolge der Elution in die Lösung unterschiedlich.
(3) Hydrophobe Chromatographie: Mithilfe der Hydrophobie von Proteinen werden hydrophobe Reste auf der Oberfläche von Proteinen nach der Denaturierung oder in einer Umgebung mit hohem Salzgehalt freigelegt. Die hydrophoben Reste verschiedener Proteine wirken unterschiedlich stark auf die hydrophoben Liganden der stationären Phase ein.
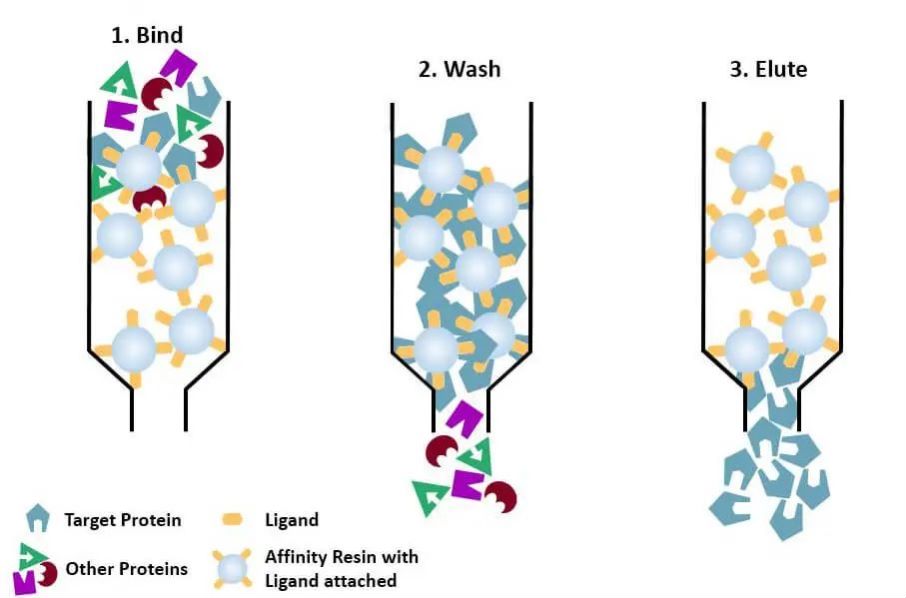
(4) Affinitätschromatographie: Der spezifische Ligand eines zu reinigenden Proteins (oder eine Markierung am Protein) wird durch geeignete chemische Methoden kovalent an das Trägermolekül gebunden. Bei Zugabe des Proteingemisches zur mit Affinitätsmedium gefüllten Chromatographiesäule wird das zu reinigende Protein spezifisch an den Liganden gebunden, während die anderen Proteine nicht gebunden und durch Waschen entfernt werden und das spezifisch gebundene Protein mit einer Lösung des freien entsprechenden Liganden eluiert werden kann. Die spezifisch gebundenen Proteine können mit einer Lösung, die den freien entsprechenden Liganden enthält, eluiert werden.
4、Auswahl der Proteinreinigungsetiketten:
Die Eigenschaften verschiedener Etiketten sind wie folgt↓
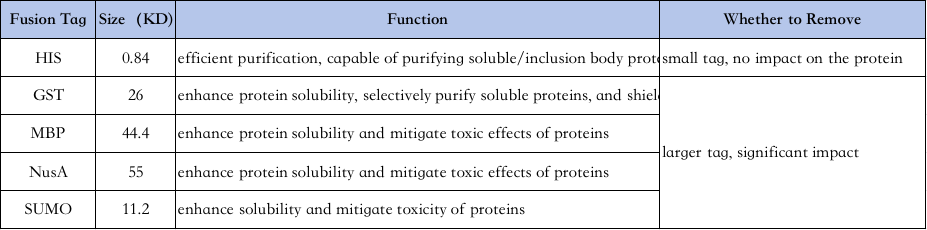
His-Tag-Reinigung: His-Tag ist einer der am häufigsten verwendeten Tags, bei dem 6–10 Histidin an den Amino- oder Carboxy-Terminus des Proteins angefügt werden und das Zielprotein durch seine Fähigkeit, unter normalen oder denaturierenden Bedingungen (z. B. 8 M Harnstoff) fest an Ni2+-Chelatsäulen zu binden, gereinigt und dann mit Imidazol (das um die Bindung an Nickelionen in den Perlenvertiefungen konkurriert) eluiert wird.
Instrumente und Verbrauchsmaterialien
Laborreagenzien:
IPTG; LB-Medium;
Lysepuffer: 20 mM Tris (7,9), 500 mM NaCl, 10 mM Imidazol;
Waschpuffer: 20 mM Tris (7,9), 500 mM NaCl, 20 mM Imidazol;
Elutionspuffer: 20 mM Tris (7.9), 200 mM NaCl, 300 mM Imidazol ( die Imidazol-Konzentration kann entsprechend der Elutionseffizienz angepasst werden );
Dialyselösung: 20 mM Tris (7,9), 50 mM NaCl, 10 % Glycerin;
Kaomas Brilliant Blue-Färbelösung; Entfärbungslösung
Instrumente:
Ni-NTA, Ultraschallbrecher, Chromatographiesäule, Konzentrationsröhrchen

Verfahren
1、Konstruktion eines prokaryotischen Expressionsplasmids: PCR des Zielgens, Vektorverdauung, Ligation, Transformation, Auswahl eines einzelnen Klons für die Sequenzierung;
2、Transformieren Sie das erfolgreich konstruierte Plasmid in BL21(DE3), inkubieren Sie es über Nacht bei 37℃ und wählen Sie den einzelnen Klon für leichtes Schütteln über Nacht aus;
3、Kleine Induktion, um die besten Induktionsbedingungen herauszufinden: Über Nacht wird die Bakterienlösung 1:1000 geschüttelt, in 3 ml LB geimpft, 37 °C, 4–5 Stunden lang geschüttelt, bis die Bakterienlösung OD600 = 0,6–0,8 ist, verschiedene Konzentrationen von IPTG (0,1–1 mM) hinzufügen, unterschiedliche Temperaturen, mit der Senkung der Temperatur verlängert sich die Induktionszeit, z. B. 37 ℃ induzierte 4-5h, 30 ℃ induzierte 6h-8h, 16 ℃ induzierte 16-20h, 16°C induzierte 16-20h, die Temperatur wird reduziert, die Zeit verlängert, wie 37 ℃ induzierte 4-5h, 30 ℃ induzierte 6h-8h, 16°C induzierte 16-20h, die Temperatur wird reduziert. 16–20 Stunden lang bei C halten, den Bakteriensaft vor und nach der Induktion unter verschiedenen Induktionsbedingungen entnehmen, das Gel laufen lassen, färben und die Ergebnisse der Induktion beobachten; (Im Allgemeinen gilt: Je niedriger die IPTG-Konzentration und je niedriger die Induktionstemperatur, desto langsamer ist die Expression des Zielproteins, desto förderlicher ist die korrekte Faltung der Proteine, wodurch ihre Löslichkeit erhöht und die Bildung von Einschlusskörpern verringert wird.)
4、Nachdem Sie die am besten geeigneten Induktionsbedingungen gefunden haben, inokulieren Sie die Bakterienlösung 1:1000 in 2 l LB, schütteln Sie bei 37 °C, bis der OD600 der Bakterienlösung = 0,6–0,8 beträgt, aspirieren Sie 20 μl der Bakterienlösung und lassen Sie das Gel laufen (1), induzieren Sie dann die Proteinexpression unter den geeigneten Induktionsbedingungen, die Sie im Vorexperiment erhalten haben, und aspirieren Sie 20 μl der Bakterienlösung und lassen Sie das Gel laufen (2);
5、Entfernen Sie die induzierte Bakterienflüssigkeit und zentrifugieren Sie sie 15 Minuten lang bei 4 °C und 4000 g.
6、Entsorgen Sie den Überstand, wiegen Sie ihn, fügen Sie 10 ml Lysepuffer (1:100 plus Proteaseinhibitor) für jedes Gramm Bakterien hinzu, resuspendieren Sie ihn und stellen Sie ihn etwa 30 Minuten lang auf Eis.
7、Druckzerkleinerung: Alkohol in den Hochdruckhomogenisator geben, zweimal mit Wasser spülen, einmal Lysepuffer zum Ausgleich verwenden, Bakterienflüssigkeit zugeben, unter Druck setzen (Druck sollte 800 kPa nicht überschreiten), die Bakterienflüssigkeit drei- bis fünfmal transparent und nicht klebrig machen;
8、Sammeln Sie die zerkleinerte Bakterienflüssigkeit, 12000 g, zentrifugieren Sie sie bei 4 °C für 20 Minuten, trennen Sie den Überstand und den Niederschlag und behalten Sie jeweils 20 μl Probe (3) (4), um das Gel laufen zu lassen;
9、2 ml Ni-NTA wurden zur Reinigungssäule gegeben, mit Ethanol filtriert, mit Wasser gespült und mit Lysepuffer versetzt, um die Säule auszugleichen.
10、Mit Lysepuffer-Ni-NTA-Resuspension zum Überstand hinzufügen, gut mischen, 2 Stunden lang bei 4 °C im Schüttler inkubieren;
11、Der Überstand wurde bei 4 °C durch die Säule geleitet und 20 μl Filtrat wurden gesammelt (5);
12、Waschen Sie die Säule dreimal mit 5 ml Waschpuffer und sammeln Sie 20 μl der Filtratprobe (6);
13、1 ml Elutionspuffer hinzufügen, 5 Minuten lang inkubieren, das Eluat auffangen, fünfmal wiederholen, 5 ml Eluat im selben Röhrchen auffangen, 20 μl Probe übrig lassen (7);
14、Die einzelnen im Verlauf des Experiments erhaltenen Proteinproben wurden getestet, 1 Stunde lang mit Caumas Brilliant Blue gefärbt und entfärbt, bis die blaue Hintergrundfarbe heller war und klare Proteinbanden sichtbar waren;
15、Analysieren Sie die Proteinbanden jeder Probe entsprechend den Ergebnissen des nachfolgenden Vorgangs: Wenn die eluierten Proteinproben im Protein keine heterozygoten Banden oder heterozygote Banden oder weniger und flach sind, kann eine Dialyse und Konzentration durchgeführt werden, wenn mehr heterozygote Banden nach der Dialyse und Konzentration erneut gereinigt werden müssen.
16、Dialyse: Geben Sie die Probe in die Dialysemembran, klemmen Sie beide Enden fest und dialysieren Sie über Nacht bei 4 °C.
17、Konzentration: Wählen Sie entsprechend der Molekulargewichtsgröße der Probe das geeignete Konzentrationsröhrchen mit 4 °C niedriger Geschwindigkeit, Konzentrationsmessung, Kennzeichnung der Proteinkonzentration, Schnellgefrieren in flüssigem Stickstoff und anschließendes Einfrieren im Kühlschrank bei -80 °C.
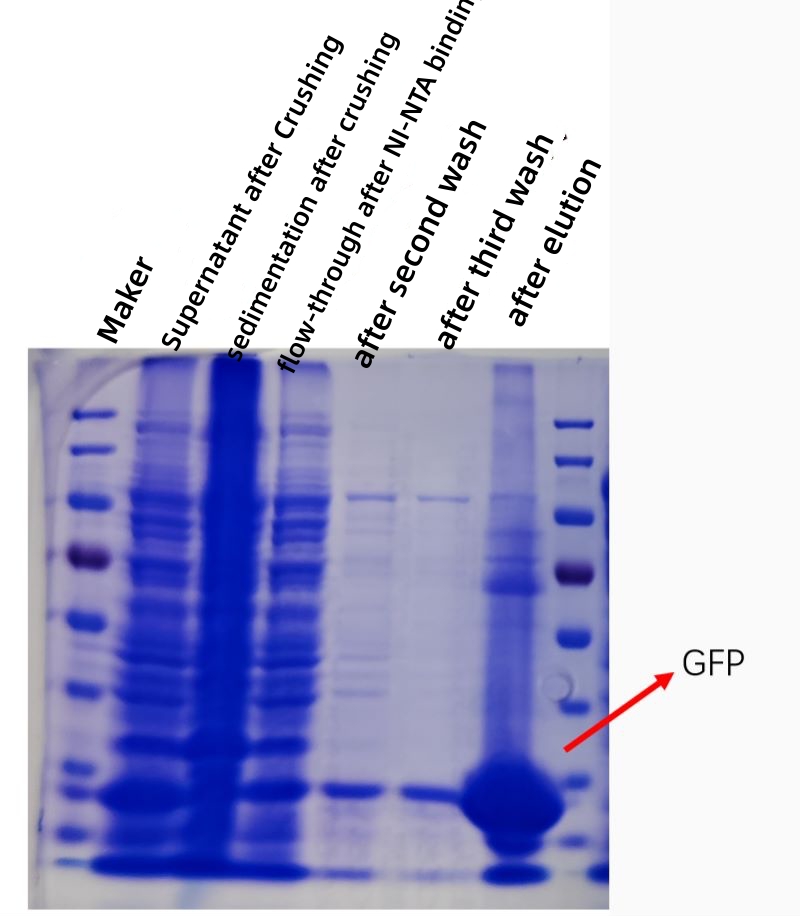
ERGEBNIS
Die folgende Abbildung zeigt ein Kofektionsdiagramm der GFP-Protein-Affinitätsreinigung in vitro, wobei die Reinheit und Konzentration des gereinigten Proteins stark erhöht wird