Oczyszczanie białek to proces wprowadzania sekwencji kwasów nukleinowych kodujących białka do komórek gospodarza za pomocą technik inżynierii genetycznej, powodując ich ekspresję w dużych ilościach, a następnie oczyszczanie ich in vitro przy użyciu odpowiednich metod oczyszczania w celu uzyskania białek o wysokiej czystości, aktywności i wydajności . Systemy ekspresji białek można podzielić na systemy prokariotyczne i systemy eukariotyczne.
zasady i metody indukowania ekspresji białek w układach prokariotycznych oraz oczyszczania białek in vitro za pomocą chromatografii powinowactwa . Poniżej opisano
ZASADA
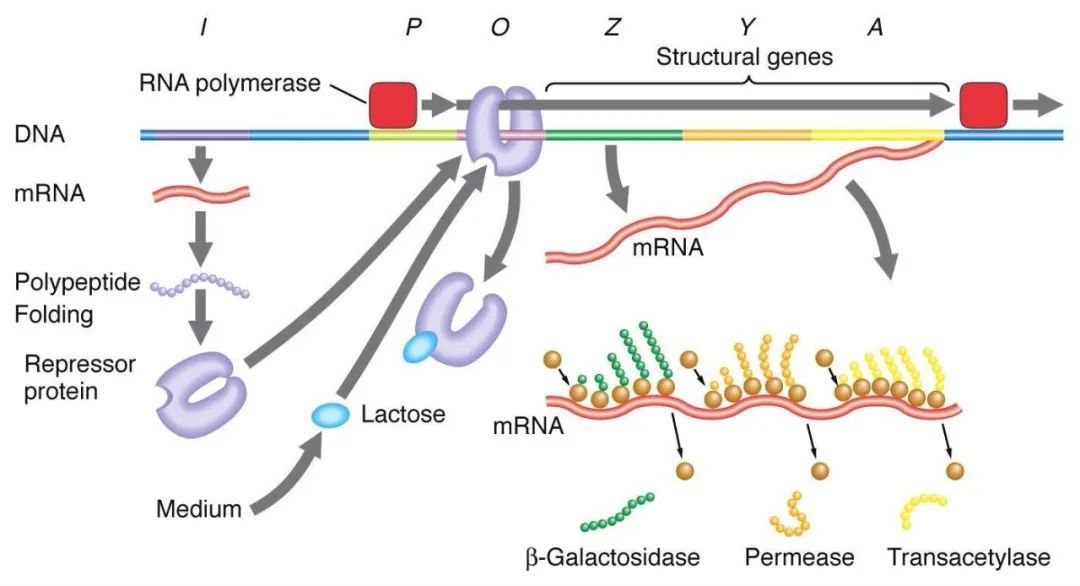
1, Negatywna regulacja manipulatora laktozy:
W przypadku braku laktozy manipulator lac znajduje się w stanie odstraszania, w którym to czasie sekwencja I wyraża białko odstraszające Lac, które wiąże się z sekwencją O, zapobiegając wiązaniu się polimerazy RNA z sekwencją P i hamując inicjację transkrypcji. Gdy laktoza jest obecna, laktoza dostaje się do komórki i jest katalizowana przez β-galaktozydazę i przekształcana w izolaktozę, która wiąże się z białkiem hamującym, powodując zmianę konformacyjną białka i prowadząc do dysocjacji białka hamującego od sekwencji O, inicjując w ten sposób transkrypcję.
Izopropylotiogalaktozyd (IPTG) działa w taki sam sposób jak izogalaktoza i jest niezwykle silnym induktorem, który nie jest metabolizowany przez bakterie i jest bardzo stabilny, dlatego jest szeroko stosowany w laboratoriach.
2. Wybór szczepu gospodarza:
(1) BL21 jest jednym z najczęściej stosowanych szczepów do ekspresji prokariotycznej, który nadaje się głównie do ekspresji nietoksycznych białek za pomocą polimerazy E. coli, dlatego może być stosowany do ekspresji układów prokariotycznych przy użyciu polimerazy RNA E. coli, takiej jak tac lub trc (np. plazmidy pGEX, pMAL).
(2) BL21(DE3) integruje gen polimerazy RNA faga T7 w regionie DE3 faga λ na chromosomie szczepu BL21, który może wyrażać zarówno polimerazę RNA T7, jak i polimerazę RNA E. coli i może być stosowany do ekspresji plazmidów, takich jak seria pET, pGEX, pMAL i tak dalej.
3, metody oczyszczania białek:
(1) Chromatografia z filtracją żelową: w zależności od wielkości cząsteczek mieszaniny do rozdzielania białek, kształtu różnych białek i wielkości cząsteczek różnic w mieszaninie przez kolumnę do chromatografii z filtracją żelową zawierającą cząstki wypełniacza, ze względu na wielkość cząsteczek różnych białek są różne, dyfuzja do określonej wielkości cząstek apertury może się zmieniać, im większe cząsteczki białka będą jako pierwsze wyeluowane z cząsteczek, tym są mniejsze, im później, tym późniejsza elucja.
(2) Chromatografia jonowymienna: rozdzielanie i oczyszczanie białek opiera się na różnych ładunkach na powierzchni białka, powierzchnia białka jest zwykle naładowana równomiernie i pod pewnymi warunkami można ją łączyć z kolumnami kationowymiennymi/anionowymiennymi. W przypadku zmiany pH lub zastosowania do elucji buforu o stopniowo rosnącej sile jonowej, związaną substancję można wymienić z jonami w eluencie i wyeluować do roztworu. Ponieważ różne substancje mają różne ładunki i różne zdolności wiązania z kolumną jonowymienną, kolejność elucji do roztworu jest również inna.
(3) Chromatografia hydrofobowa: Wykorzystując hydrofobowość białek, reszty hydrofobowe zostaną odsłonięte na powierzchni białek po denaturacji lub w środowisku o wysokiej zawartości soli, reszty hydrofobowe różnych białek mają różną siłę działania z hydrofobowymi ligandami fazy stacjonarnej, a hydrofobowość można zastosować jako rozdział od najsłabszego do najsilniejszego składnika, stosując siłę jonową eluentu w kolejności od wysokiej do niskiej.
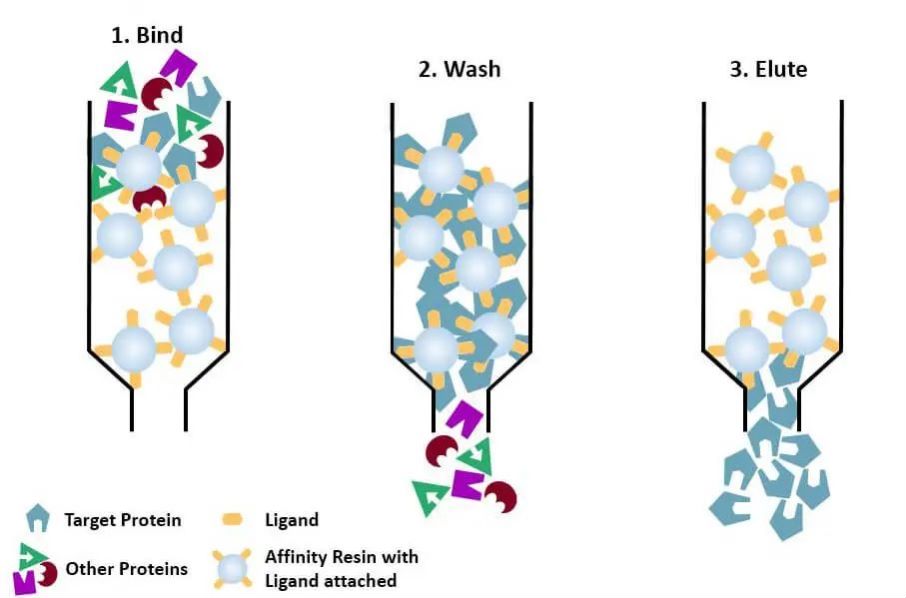
(4) Chromatografia powinowactwa: specyficzny ligand białka, które ma zostać oczyszczone (lub znakowane na białku), jest kowalencyjnie przyłączany do cząsteczki nośnika odpowiednimi metodami chemicznymi. Gdy mieszaninę białek dodaje się do kolumny chromatograficznej wypełnionej ośrodkiem powinowactwa, oczyszczane białko jest specyficznie związane z ligandem, podczas gdy inne białka nie są wiązane i usuwane przez przemywanie, a specyficznie związane białko można eluować roztworem wolnego odpowiedniego ligandu. Specyficznie związane białka można eluować roztworem zawierającym wolny odpowiedni ligand.
4、Wybór etykiet do oczyszczania białek:
Charakterystyka różnych etykiet jest następująca↓
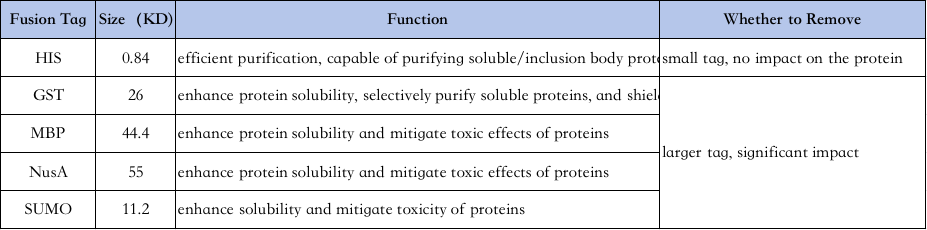
Oczyszczanie znacznika His: znacznik His jest jednym z najczęściej używanych znaczników, w którym do końca aminowego lub karboksylowego białka dodaje się 6-10 histydyny, a białko docelowe oczyszcza się poprzez jego zdolność do ścisłego wiązania się z kolumnami chelatującymi Ni2+ w normalnych lub denaturujących warunkach (np. 8M mocznik), a następnie eluuje imidazolem (który konkuruje o wiązanie z jonami niklu w dołkach kulek).
Instrumenty i materiały eksploatacyjne
Odczynniki laboratoryjne:
IPTG; średni LB;
Bufor do lizy: 20 mM Tris (7.9), 500 mM NaCl, 10 mM imidazol;
Bufor płuczący: 20 mM Tris (7.9), 500 mM NaCl, 20 mM imidazol;
Bufor do elucji: 20 mM Tris (7,9), 200 mM NaCl, 300 mM imidazol ( stężenie imidazolu można dostosować w zależności od wydajności elucji );
Roztwór do dializy: 20 mM Tris (7,9), 50 mM NaCl, 10% glicerol;
Roztwór barwiący Kaomas Brilliant Blue; roztwór odbarwiający
Instrumenty:
Ni-NTA, wyłącznik ultradźwiękowy, kolumna chromatograficzna, probówki zatężające

Procedura
1. Konstrukcja prokariotycznego plazmidu ekspresyjnego: PCR genu docelowego, trawienie wektora, ligacja, transformacja, wybór pojedynczego klonu do sekwencjonowania;
2、Przekształć pomyślnie skonstruowany plazmid w BL21(DE3), inkubuj w temperaturze 37℃ przez noc i wybierz pojedynczy klon do małego wytrząsania przez noc;
3. Mała indukcja, aby znaleźć najlepsze warunki indukcji: roztwór bakteryjny będzie wstrząśnięty przez noc. Zaszczepienie 1:1000 do 3 ml LB, 37 ℃ wytrząsanie przez 4-5 godzin do roztworu bakteryjnego OD600 = 0,6-0,8, dodanie różnych stężeń IPTG (0,1-1 mM), różnych temperatur, wraz z obniżeniem temperatury czas indukcji wydłuża się, np. 37 ℃ indukowane 4-5h, 30℃ indukowane 6h-8h, 16℃ indukowane 16-20h, 16°C indukowane 16-20h, temperatura jest obniżana, czas wydłużany, np. 37℃ indukowany 4-5h, 30℃ indukowany 6h-8h, 16°C indukowany 16-20h, temperatura jest obniżona. C przez 16-20h, pobrać sok bakteryjny przed i po indukcji w różnych warunkach indukcji, rozpuścić żel, wybarwić i obserwować rezultaty indukcji; (Generalnie im niższe stężenie IPTG i im niższa temperatura indukcji, tym wolniejsza ekspresja docelowego białka, tym lepiej sprzyja prawidłowemu zwijaniu białek, zwiększając tym samym ich rozpuszczalność i ograniczając powstawanie ciał inkluzyjnych)
4、Po znalezieniu najbardziej odpowiednich warunków indukcji zaszczepić roztwór bakterii w proporcji 1:1000 do 2L LB, wstrząsać w temperaturze 37℃ aż do uzyskania OD600 roztworu bakterii = 0,6-0,8, zaaspirować 20µl roztworu bakterii i pozostawić do przepuszczenia żelu (1), następnie wywołać ekspresję białka w odpowiednich warunkach indukcji uzyskanych w eksperymencie wstępnym i zaaspirować 20µL roztworu bakteryjnego i pozostawić do wchłonięcia żelu (2);
5、Usunąć indukowany płyn bakteryjny, odwirować przy 4000g przez 15min w 4℃;
6、Odrzucić supernatant, zważyć, dodać 10 ml buforu lizującego (1:100 plus inhibitor proteazy) na każdy gram bakterii, ponownie zawiesić, umieścić na lodzie na około 30 minut;
7, Kruszenie ciśnieniowe: odstawić alkohol do homogenizatora wysokociśnieniowego, dwukrotnie przepłukać wodą, jednokrotnie użyć buforu lizującego do zrównoważenia, dodać płyn bakteryjny, zwiększyć ciśnienie (ciśnienie nie powinno przekraczać 800 kpa), płyn bakteryjny trzy do pięciu razy, aby stał się przezroczysty i niekleisty;
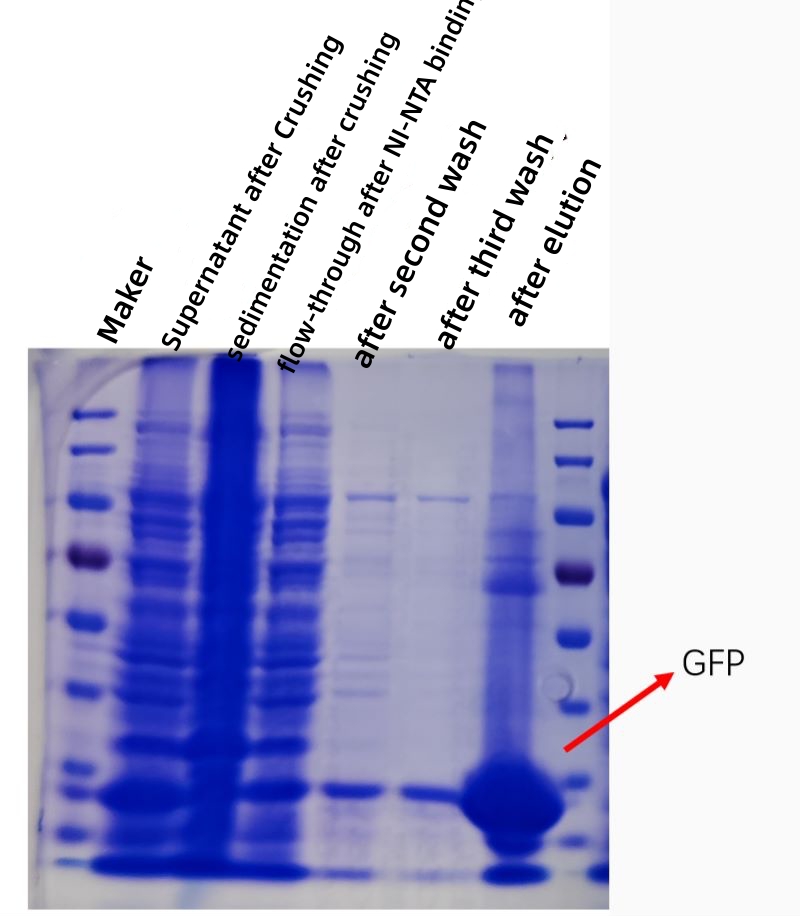
8. Zbierz rozdrobniony płyn bakteryjny, 12000 g, wiruj w temperaturze 4 ℃ przez 20 minut, oddziel supernatant i osad, każda zatrzymana próbka 20 μL (3) (4) do analizy żelu;
Do kolumny oczyszczającej dodano 9, 2 ml Ni-NTA, przesączono przez etanol, przepłukano wodą i dodano bufor lizujący w celu zrównoważenia kolumny;
10. Do supernatantu dodać bufor lizujący Ni-NTA, dobrze wymieszać i inkubować na wytrząsarce w temperaturze 4 ℃ przez 2 godziny;
11. Supernatant przepuszczono przez kolumnę w temperaturze 4°C i zebrano 20 µl przesączu (5);
12. Przemyj kolumnę 3 razy 5 ml buforu płuczącego, zbierz próbkę filtratu 20 μL (6);
13. Dodaj 1 ml buforu do elucji, inkubuj przez 5 minut, zbierz eluat, powtórz 5 razy, zbierz 5 ml eluatu do tej samej probówki, pozostaw 20 μL próbki (7);
14. Poszczególne próbki białek uzyskane w trakcie doświadczenia poddano analizie, barwiono błękitem brylantowym Caumas przez 1 godzinę i odbarwiano do momentu, aż niebieski kolor tła stał się jaśniejszy i widoczne były wyraźne prążki białka;
15. Przeanalizuj prążki białkowe w każdej próbce, zgodnie z wynikami kolejnych operacji: jeśli wymyte próbki białka w białku bez prążków heterozygotycznych lub prążków heterozygotycznych lub są mniejsze i płytkie, można poddać dializie i zatężeniu, jeśli po dializie i zatężeniu należy ponownie oczyścić więcej prążków heterozygotycznych.
16. Dializa: dodać próbkę do membrany dializacyjnej, zacisnąć oba końce, dializa w temperaturze 4℃ przez noc;
17, Stężenie: w zależności od masy cząsteczkowej próbki wybrać odpowiednią probówkę do pomiaru stężenia 4 ℃ przy niskiej prędkości, pomiar stężenia białka, etykietowanie, szybkie zamrażanie w ciekłym azocie, a następnie zamrożenie w lodówce -80 ℃.
WYNIK
Poniższy rysunek przedstawia wykres kofekcji oczyszczania białka GFP na podstawie powinowactwa in vitro, przy czym czystość i stężenie oczyszczonego białka są znacznie zwiększone