La purificazione delle proteine è il processo di introduzione di sequenze di acido nucleico che codificano per proteine nelle cellule ospiti attraverso tecniche di ingegneria genetica, facendole esprimere in grandi quantità, e quindi purificandole in vitro utilizzando metodi di purificazione appropriati al fine di ottenere proteine di elevata purezza, attività e resa . I sistemi di espressione proteica possono essere classificati in sistemi procariotici e sistemi eucariotici.
I principi e i metodi per indurre l'espressione proteica nei sistemi procariotici e purificare le proteine in vitro utilizzando la cromatografia di affinità sono descritti di seguito.
PRINCIPIO
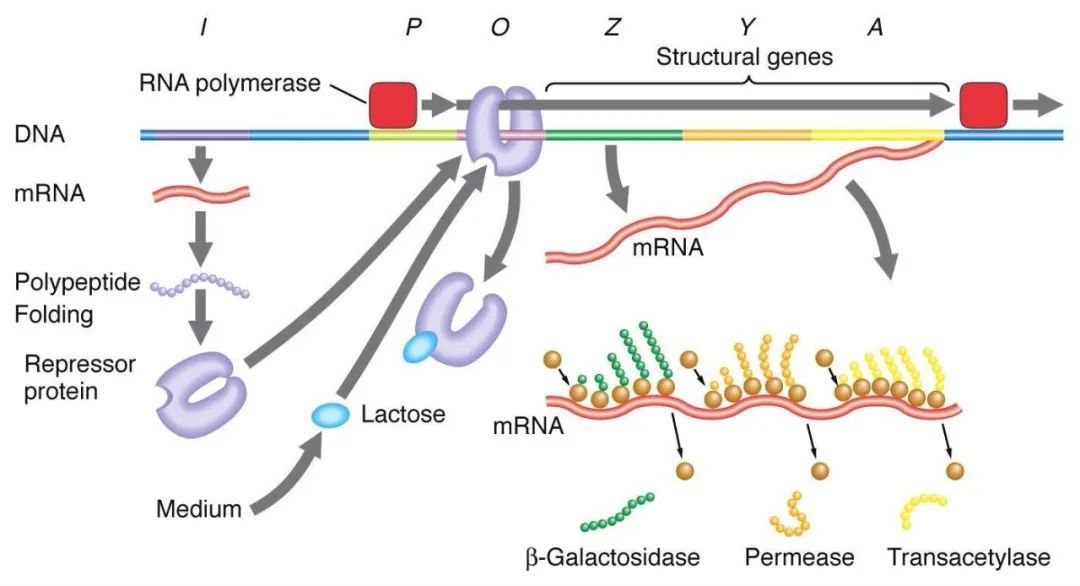
1、Regolazione negativa del manipolatore del lattosio:
In assenza di lattosio, il manipolatore lac è in uno stato di deterrenza, momento in cui la sequenza I esprime la proteina deterrente Lac per legarsi alla sequenza O, impedendo alla RNA polimerasi di legarsi alla sequenza P e inibendo l'inizio della trascrizione. Quando è presente, il lattosio entra nella cellula e viene catalizzato dalla β-galattosidasi e convertito in isolattosio, che si lega alla proteina inibitrice, provocando un cambiamento conformazionale nella proteina e portando alla dissociazione della proteina inibitrice dalla sequenza O, iniziando così la trascrizione.
L'isopropiltiogalattoside (IPTG) agisce allo stesso modo dell'isogalattosio ed è un induttore estremamente potente che non viene metabolizzato dai batteri ed è molto stabile, ed è quindi ampiamente utilizzato nei laboratori.
2、selezione del ceppo ospite:
(1) BL21 è uno dei ceppi più comunemente utilizzati per l'espressione procariotica, che è adatto principalmente per l'espressione di proteine non tossiche con la polimerasi di E. coli, quindi può essere applicato all'espressione di sistemi procariotici utilizzando la RNA polimerasi di E. coli come tac o trc (ad esempio pGEX, plasmidi pMAL).
(2) BL21(DE3) integra il gene della RNA polimerasi del fago T7 nella regione DE3 del fago λ sul cromosoma del ceppo BL21, che può esprimere sia la RNA polimerasi T7 che la RNA polimerasi di E. coli e può essere utilizzato per l'espressione di plasmidi come la serie pET, pGEX, pMAL e così via.
3, metodi di purificazione delle proteine:
(1) Cromatografia con filtrazione su gel: in base alla dimensione molecolare della miscela per separare le proteine, alla forma delle diverse proteine e alla dimensione molecolare delle differenze nella miscela attraverso la colonna per cromatografia a filtrazione su gel contenente particelle di riempimento, a causa della dimensione molecolare delle varie proteine sono diverse, la diffusione nella dimensione specifica delle particelle di apertura della capacità di variare, più grandi le molecole proteiche saranno le prime ad essere eluite dalle molecole più piccole più tardi sarà l'eluizione.
(2) Cromatografia a scambio ionico: la separazione e purificazione delle proteine si basa sulle diverse cariche sulla superficie della proteina, la superficie della proteina è solitamente caricata in modo uniforme e può essere combinata con colonne a scambio cationico/anione in determinate condizioni. Quando il pH viene modificato o per l'eluizione viene utilizzato un tampone con forza ionica gradualmente crescente, la sostanza legata può essere scambiata con gli ioni nell'eluente ed eluita nella soluzione. Poiché sostanze diverse hanno cariche diverse e capacità di legame diverse con la colonna a scambio ionico, anche l'ordine di eluizione nella soluzione è diverso.
(3) Cromatografia idrofobica: utilizzando l'idrofobicità delle proteine, i residui idrofobici verranno esposti sulla superficie delle proteine dopo la denaturazione o in un ambiente ad alto contenuto salino, i residui idrofobici di diverse proteine hanno diversi punti di forza d'azione con i ligandi idrofobici della fase stazionaria e l'idrofobicità può essere utilizzata come separazione dei componenti dal più debole al più forte utilizzando la forza ionica dell'eluente in ordine da alta a bassa.
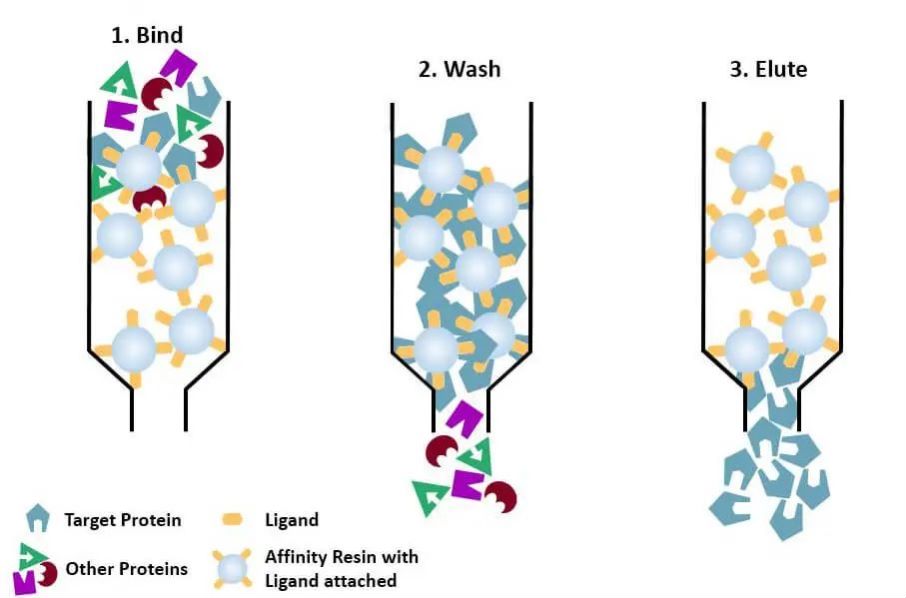
(4) Cromatografia di affinità: il ligando specifico di una proteina da purificare (o marcato sulla proteina) è legato covalentemente alla molecola trasportatrice mediante metodi chimici appropriati. Quando la miscela proteica viene aggiunta alla colonna cromatografica riempita con mezzo di affinità, la proteina da purificare è legata in modo specifico al ligando, mentre le altre proteine non vengono legate e rimosse mediante lavaggio, e la proteina legata in modo specifico può essere eluita con una soluzione di ligando corrispondente libero. Le proteine specificatamente legate possono essere eluite con una soluzione contenente il corrispondente ligando libero.
4、Selezione delle etichette per la purificazione delle proteine:
Le caratteristiche delle diverse etichette sono le seguenti↓
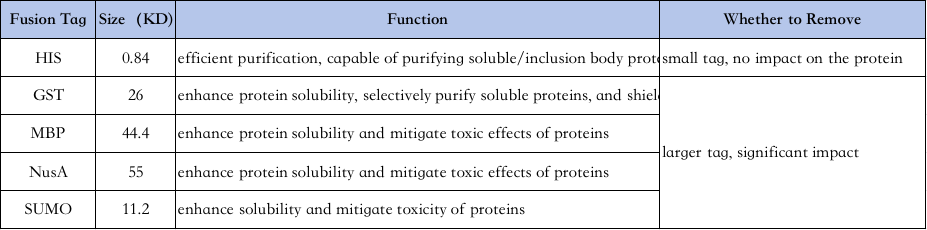
Purificazione con His-tag: His-tag è uno dei tag più comunemente utilizzati, in cui 6-10 istidina vengono aggiunte all'estremità amminica o carbossilica della proteina e la proteina bersaglio viene purificata grazie alla sua capacità di legarsi saldamente alle colonne chelanti Ni2+ in condizioni normali o denaturanti (ad esempio, urea 8M) e quindi eluita con imidazolo (che compete per il legame con gli ioni nichel nei pozzetti delle sfere).
Strumenti e materiali di consumo
Reagenti di laboratorio:
IPTG; LB medio;
Tampone di lisi: Tris 20 mM (7.9), NaCl 500 mM, Imidazolo 10 mM;
Tampone di lavaggio: Tris 20 mM (7.9), NaCl 500 mM, Imidazolo 20 mM;
Tampone di eluizione: Tris (7.9) 20 mM, NaCl 200 mM, Imidazolo 300 mM ( la concentrazione di imidazolo può essere regolata in base all'efficienza di eluizione );
Soluzione di dialisi: Tris 20 mM (7.9), NaCl 50 mM, glicerolo al 10%;
Soluzione colorante Kaomas Brilliant Blue; soluzione decolorante
Strumenti:
Ni-NTA, interruttore ad ultrasuoni, colonna per cromatografia, tubi di concentrazione

Procedura
1、Costruzione del plasmide di espressione procariotica: PCR del gene bersaglio, digestione del vettore, legatura, trasformazione, selezione di un singolo clone per il sequenziamento;
2、Trasformare il plasmide costruito con successo in BL21(DE3), incubare a 37℃ durante la notte e selezionare il singolo clone per un piccolo scuotimento durante la notte;
3、Piccola induzione per individuare le migliori condizioni di induzione: la soluzione batterica verrà agitata durante la notte per inoculazione 1:1000 in 3 ml di LB, 37 ℃ agitando per 4-5 ore fino alla soluzione batterica OD600 = 0,6-0,8, aggiungere diverse concentrazioni di IPTG (0,1-1 mM), diverse temperature, con l'abbassamento della temperatura, il tempo di induzione viene prolungato, ad esempio 37 ℃ indotto 4-5h, 30 ℃ indotto 6h-8h, 16 ℃ indotto 16-20h, 16 °C indotto 16-20h, la temperatura è ridotta, il tempo è esteso, come 37 ℃ indotto 4-5h, 30 ℃ indotto 6h-8h, 16 °C indotto 16-20h, la temperatura è ridotto. C per 16-20 ore, prendere la linfa batterica prima e dopo l'induzione in diverse condizioni di induzione, far funzionare il gel, colorare e osservare i risultati dell'induzione; (In generale, minore è la concentrazione di IPTG e più bassa la temperatura di induzione, più lenta è l'espressione della proteina bersaglio, più favorevole al corretto ripiegamento delle proteine, aumentando così la loro solubilità e riducendo la generazione di corpi di inclusione)
4、Dopo aver trovato le condizioni di induzione più adatte, inoculare la soluzione batterica 1:1000 in 2L di LB, agitare a 37℃ fino a OD600 della soluzione batterica = 0,6-0,8, aspirare 20μL di soluzione batterica e lasciare agire il gel (1), quindi indurre l'espressione proteica nelle condizioni di induzione adeguate ottenute nel pre-esperimento e aspirare 20μL di soluzione batterica e lasciare scorrere il gel (2);
5、Rimuovere il liquido batterico indotto, centrifugare a 4000 g per 15 minuti a 4℃;
6、Eliminare il surnatante, pesare, aggiungere 10 ml di tampone di lisi (1:100 più inibitore della proteasi) per ogni grammo di batteri, risospendere e riporre in ghiaccio per circa 30 minuti;
7、 Frantumazione a pressione: eliminare l'alcol nell'omogeneizzatore ad alta pressione, sciacquare con acqua due volte, utilizzare il tampone di lisi per bilanciare una volta, aggiungere il liquido batterico, pressurizzare (la pressione non deve superare 800 kpa), il liquido batterico da tre a cinque volte fino a renderlo trasparente e non appiccicoso;
8、Raccogliere il liquido batterico frantumato, 12.000 g, centrifugazione a 4 ℃ per 20 minuti, separazione del surnatante e del precipitato, ciascun campione trattenuto da 20μL (3) (4) da utilizzare come gel;
Alla colonna di purificazione sono stati aggiunti 9,2 ml di Ni-NTA, per essere filtrati con etanolo, risciacquati con acqua e aggiunto tampone di lisi per equilibrare la colonna;
10、Con la risospensione del tampone di lisi Ni-NTA aggiunta al surnatante, mescolare bene e incubare in agitatore a 4 ℃ per 2 ore;
11、Il surnatante è stato fatto passare attraverso la colonna a 4°C e sono stati raccolti 20 μL di filtrato (5);
12、Lavare la colonna con 5 ml di tampone di lavaggio 3 volte, raccogliere il campione filtrato 20μL (6);
13、Aggiungere 1 ml di tampone di eluizione, incubare per 5 minuti, raccogliere l'eluato, ripetere 5 volte, raccogliere 5 ml di eluato nella stessa provetta, lasciare 20μL di campione (7);
14、I singoli campioni proteici ottenuti nel corso dell'esperimento sono stati analizzati, colorati con Caumas Brilliant Blue per 1 ora e decolorati fino a quando il colore blu dello sfondo era più chiaro e erano visibili bande proteiche chiare;
15、Analizzare le bande proteiche di ciascun campione, in base ai risultati dell'operazione successiva: se i campioni proteici eluiti nella proteina senza bande eterozigoti o bande eterozigoti o meno e superficiali, possono essere dialisi e concentrazione, se più bande eterozigoti devono essere purificate nuovamente dopo la dialisi e la concentrazione.
16、Dialisi: aggiungere il campione nella membrana di dialisi, bloccare entrambe le estremità, dialisi a 4℃ durante la notte;
17、Concentrazione: in base alla dimensione del peso molecolare del campione, scegliere la provetta di concentrazione appropriata a 4 ℃ concentrazione a bassa velocità, concentrazione della concentrazione proteica, misurazione, etichettatura, congelamento rapido in azoto liquido e quindi congelamento in frigorifero a -80 ℃.
RISULTATO
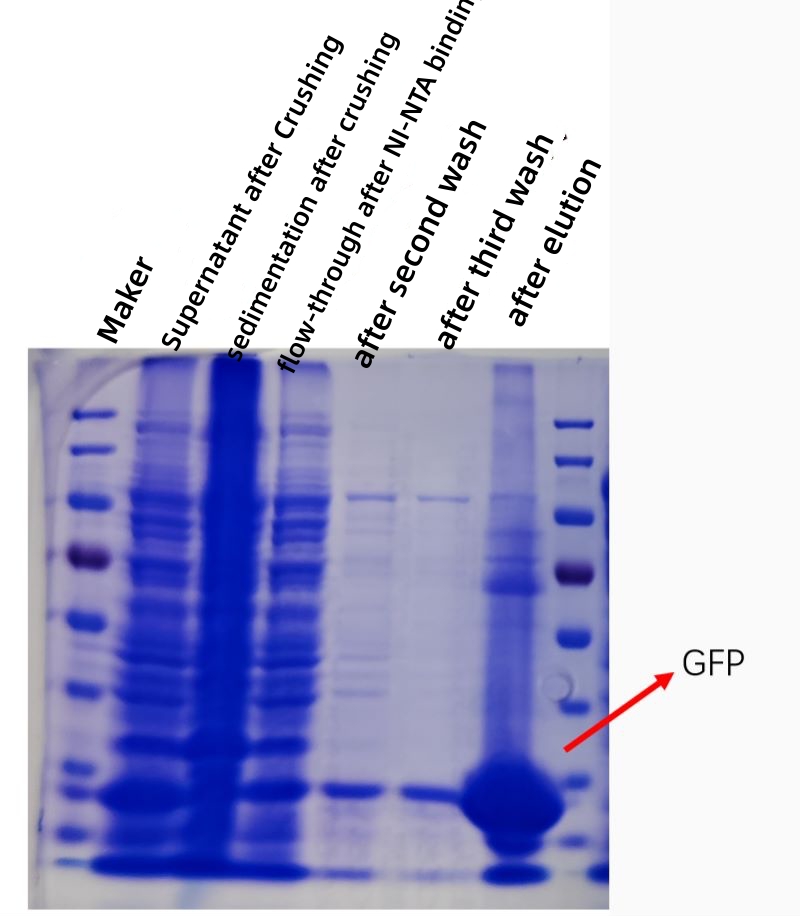
La figura seguente mostra un grafico di kofection della purificazione per affinità proteica GFP in vitro e la purezza e la concentrazione della proteina purificata sono notevolmente aumentate