La purification des protéines est le processus d'introduction de séquences d'acide nucléique codant pour des protéines dans les cellules hôtes par le biais de techniques de génie génétique, provoquant leur expression en grande quantité, puis de leur purification in vitro à l'aide de méthodes de purification appropriées afin d'obtenir des protéines de haute pureté, activité et rendement . Les systèmes d'expression des protéines peuvent être classés en systèmes procaryotes et systèmes eucaryotes..
Les principes et les méthodes permettant d'induire l'expression de protéines dans des systèmes procaryotes et de purifier des protéines in vitro par chromatographie d'affinité sont décrits ci-dessous.
PRINCIPE
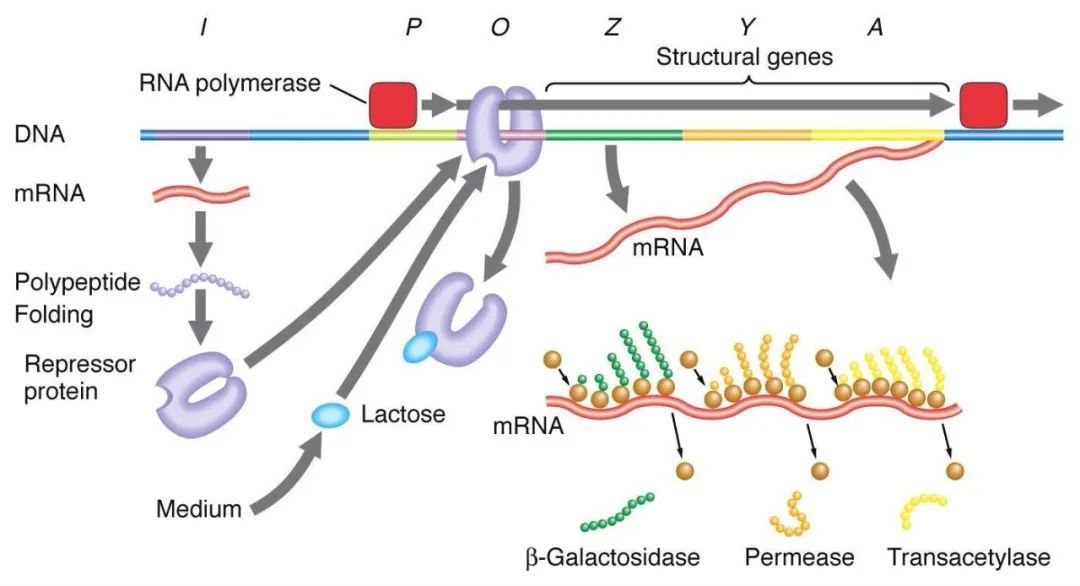
1. Régulation négative du manipulateur de lactose :
En l'absence de lactose, le manipulateur lac est dans un état de dissuasion, moment auquel la séquence I exprime la protéine dissuasive Lac pour se lier à la séquence O, empêchant l'ARN polymérase de se lier à la séquence P et inhibant l'initiation de la transcription. Lorsque le lactose est présent, le lactose pénètre dans la cellule et est catalysé par la β-galactosidase et converti en isolactose, qui se lie à la protéine inhibitrice, provoquant un changement conformationnel de la protéine et conduisant à la dissociation de la protéine inhibitrice de la séquence O, initiant ainsi la transcription.
L'isopropylthiogalactoside (IPTG) agit de la même manière que l'isogalactose et constitue un inducteur extrêmement puissant, non métabolisé par les bactéries et très stable, et est donc largement utilisé en laboratoire.
2. Sélection de la souche hôte :
(1) BL21 est l'une des souches les plus couramment utilisées pour l'expression procaryote, qui convient principalement à l'expression de protéines non toxiques avec la polymérase d'E. coli, elle peut donc être appliquée à l'expression de systèmes procaryotes utilisant l'ARN polymérase d'E. coli telle que tac ou trc (par exemple les plasmides pGEX, pMAL).
(2) BL21 (DE3) intègre le gène de l'ARN polymérase du phage T7 dans la région DE3 du phage λ sur le chromosome de la souche BL21, qui peut exprimer à la fois l'ARN polymérase T7 et l'ARN polymérase d'E. coli , et peut être utilisée pour l'expression de plasmides tels que la série pET, pGEX, pMAL, etc.
3, méthodes de purification des protéines :
(1) Chromatographie de filtration sur gel : selon la taille moléculaire du mélange pour séparer les protéines, la forme des différentes protéines et la taille moléculaire des différences dans le mélange à travers la colonne de chromatographie de filtration sur gel contenant des particules de charge, en raison de la taille moléculaire de diverses protéines sont différentes, la diffusion dans la taille spécifique des particules d'ouverture de la capacité de varier, plus les molécules de protéines seront les premières à être éluées hors des molécules sont plus petites, plus l'élution est tardive.
(2) Chromatographie par échange d'ions : la séparation et la purification des protéines sont basées sur les différentes charges à la surface de la protéine, la surface de la protéine est généralement chargée de manière uniforme et peut être combinée avec des colonnes échangeuses de cations/anions dans certaines conditions. Lorsque le pH est modifié ou qu'un tampon dont la force ionique augmente progressivement est utilisé pour l'élution, la substance liée peut être échangée avec les ions de l'éluant et éluée dans la solution. Étant donné que différentes substances ont des charges différentes et des capacités de liaison différentes avec la colonne échangeuse d'ions, l'ordre d'élution en solution est également différent.
(3) Chromatographie hydrophobe : en utilisant l'hydrophobicité des protéines, les résidus hydrophobes seront exposés à la surface des protéines après dénaturation ou dans un environnement riche en sel, les résidus hydrophobes de différentes protéines ont différentes forces d'action avec les ligands hydrophobes de la phase stationnaire, et l'hydrophobicité peut être utilisée comme séparation des composants du plus faible au plus fort en utilisant la force ionique de l'éluant dans l'ordre de haut en bas.
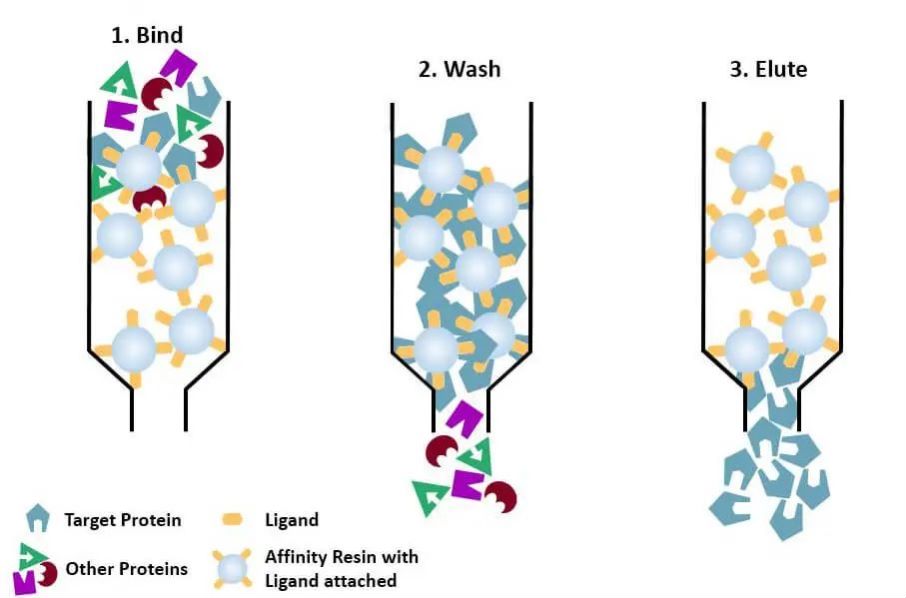
(4) Chromatographie d'affinité : le ligand spécifique d'une protéine à purifier (ou marqué sur la protéine) est attaché de manière covalente à la molécule porteuse par des méthodes chimiques appropriées. Lorsque le mélange de protéines est ajouté à la colonne chromatographique remplie de milieu d'affinité, la protéine à purifier est spécifiquement liée au ligand, tandis que les autres protéines ne sont pas liées et éliminées par lavage, et la protéine spécifiquement liée peut être éluée avec une solution de ligand correspondant libre. Les protéines spécifiquement liées peuvent être éluées avec une solution contenant le ligand libre correspondant.
4、Sélection des étiquettes de purification des protéines :
Les caractéristiques des différents labels sont les suivantes↓
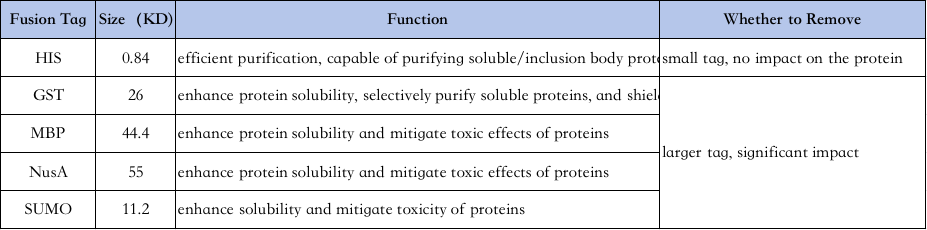
Purification de l'étiquette His : L'étiquette His-tag est l'une des étiquettes les plus couramment utilisées, où 6 à 10 histidines sont ajoutées à l'extrémité amino ou carboxyle de la protéine, et la protéine cible est purifiée par sa capacité à se lier étroitement aux colonnes chélatantes Ni2+ dans des conditions normales ou dénaturantes (par exemple, urée 8 M), puis éluée avec de l'imidazole (qui entre en compétition pour la liaison aux ions nickel dans les puits à billes).
Instruments et consommables
Réactifs de laboratoire :
IPTG; Médium LB ;
Tampon de lyse : Tris 20 mM (7,9), NaCl 500 mM, Imidazole 10 mM ;
Tampon de lavage : Tris 20 mM (7,9), NaCl 500 mM, Imidazole 20 mM ;
Tampon d'élution : Tris 20 mM (7,9), NaCl 200 mM, Imidazole 300 mM ( la concentration d'imidazole peut être ajustée en fonction de l'efficacité de l'élution ) ;
Solution de dialyse : Tris 20 mM (7,9), NaCl 50 mM, glycérol à 10 % ;
Solution de coloration Kaomas Brilliant Blue ; solution décolorante
Instruments :
Ni-NTA, brise-ultrasons, colonne de chromatographie, tubes de concentration

Procédure
1. Construction du plasmide d'expression procaryote : PCR du gène cible, digestion du vecteur, ligature, transformation, sélection d'un clone unique pour le séquençage ;
2. Transformez le plasmide construit avec succès en BL21 (DE3), incubez à 37 ℃ pendant la nuit et choisissez le clone unique pour une petite agitation pendant la nuit ;
3. Petite induction pour connaître les meilleures conditions d'induction : la solution bactérienne sera secouée pendant la nuit, inoculation 1: 1000 dans 3 ml de LB, 37 ℃ en agitant 4 à 5 h jusqu'à la solution bactérienne OD600 = 0,6-0,8, ajouter différentes concentrations d'IPTG (0,1-1 mM), différentes températures, avec l'abaissement de la température, le temps d'induction est prolongé, comme 37 ℃ induit 4-5h, 30 ℃ induit 6h-8h, 16 ℃ induit 16-20h, 16°C induit 16-20h, la température est réduite, le temps est prolongé, comme 37 ℃ induit 4-5h, 30 ℃ induit 6h-8h, 16°C induit 16-20h, la température est réduite. C pendant 16-20h, prélever la sève bactérienne avant et après induction dans différentes conditions d'induction, exécuter le gel, colorer et observer les résultats de l'induction ; (D'une manière générale, plus la concentration d'IPTG et la température d'induction sont basses, plus l'expression de la protéine cible est lente, plus elle est propice au repliement correct des protéines, augmentant ainsi leur solubilité et réduisant la génération de corps d'inclusion)
4. Après avoir trouvé les conditions d'induction les plus appropriées, inoculez la solution bactérienne 1: 1000 dans 2 L de LB, agitez à 37 ℃ jusqu'à ce que la DO600 de la solution bactérienne = 0,6-0,8, aspirez 20 μL de la solution bactérienne et laissez couler le gel (1), puis induisez l'expression de la protéine dans les conditions d'induction appropriées obtenues dans la pré-expérience, et aspirez 20 μL de la solution bactérienne et laissez-la. faire couler le gel (2) ;
5. Retirez le liquide bactérien induit, centrifugez à 4 000 g pendant 15 minutes à 4 ℃ ;
6. Jetez le surnageant, pesez, ajoutez 10 ml de tampon de lyse (1: 100 plus inhibiteur de protéase) pour chaque gramme de bactérie, remettez en suspension, placez sur la glace pendant environ 30 minutes ;
7. Broyage sous pression : mettez l'alcool dans l'homogénéisateur à haute pression, rincez à l'eau deux fois, utilisez le tampon de lyse pour équilibrer une fois, ajoutez le liquide bactérien, pressurisation (la pression ne doit pas dépasser 800 kpa), le liquide bactérien trois à cinq fois pour devenir transparent et non collant ;
8. Recueillir le liquide bactérien broyé, 12 000 g, centrifugation à 4 ℃ pendant 20 min, séparation du surnageant et du précipité, chacun conservant 20 μL d'échantillon (3) (4) à exécuter sur gel ;
9,2 ml de Ni-NTA ont été ajoutés à la colonne de purification, filtrés à l'éthanol, rincés à l'eau et ajoutés du tampon de lyse pour équilibrer la colonne ;
10. Avec la remise en suspension du tampon de lyse Ni-NTA ajoutée au surnageant, bien mélanger, incubation dans un shaker à 4 ℃ pendant 2 h ;
11. Le surnageant a été passé à travers la colonne à 4°C et 20 μL de filtrat ont été collectés (5) ;
12. Laver la colonne avec 5 ml de tampon de lavage 3 fois, collecter l'échantillon de filtrat 20 µL (6) ;
13. Ajoutez 1 ml de tampon d'élution, incubez pendant 5 minutes, collectez l'éluat, répétez 5 fois, collectez 5 ml d'éluat dans le même tube, laissez 20 µL d'échantillon (7) ;
14. Les échantillons de protéines individuels obtenus au cours de l'expérience ont été analysés, colorés au Caumas Brilliant Blue pendant 1 h et décolorés jusqu'à ce que la couleur bleue de fond soit plus claire et que des bandes de protéines claires soient visibles ;
15. Analysez les bandes protéiques de chaque échantillon, en fonction des résultats de l'opération ultérieure : si les échantillons de protéines élues dans la protéine sans bandes hétérozygotes ou bandes hétérozygotes ou moins et peu profondes, peuvent être dialyse et concentration, si des bandes plus hétérozygotes doivent être à nouveau purifiées après dialyse et concentration.
16. Dialyse : ajoutez l'échantillon dans la membrane de dialyse, fixez les deux extrémités, dialyse à 4 ℃ pendant la nuit ;
17. Concentration: en fonction de la taille du poids moléculaire de l'échantillon, choisir le tube de concentration approprié, concentration à basse vitesse de 4 ℃, mesure de la concentration en protéines, étiquetage, congélation rapide à l'azote liquide, puis congelée dans un réfrigérateur à-80 ℃.
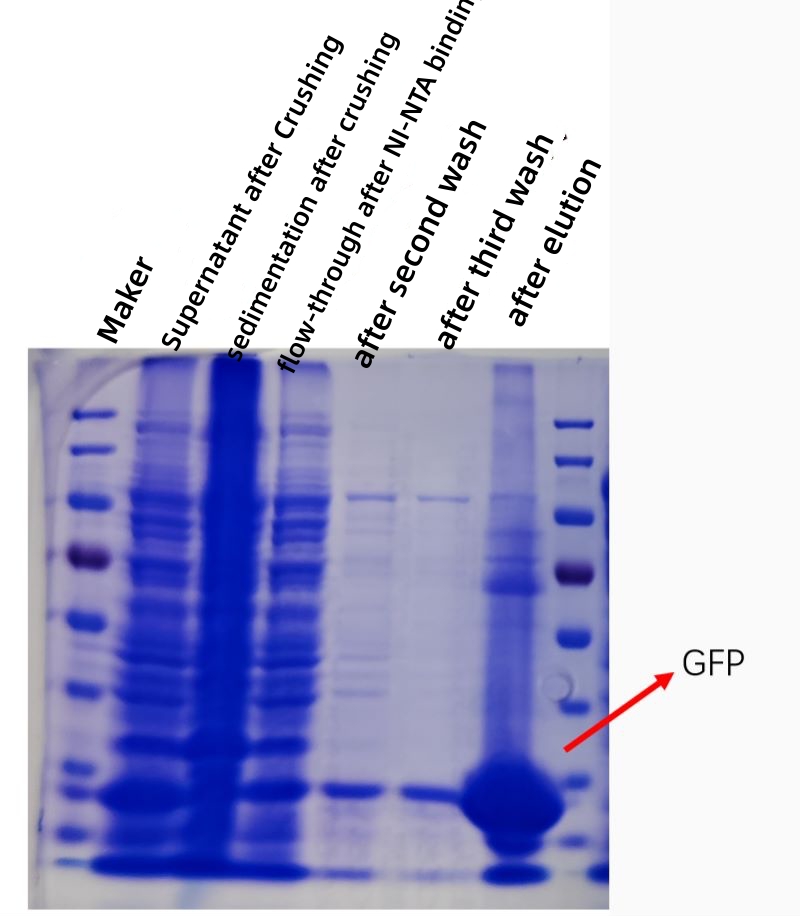
RÉSULTAT
La figure ci-dessous montre un tracé de kofection de la purification par affinité de la protéine GFP in vitro, et la pureté et la concentration de la protéine purifiée sont considérablement augmentées.